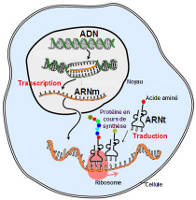
Chez les procaryotes, un gène est défini structurellement comme une séquence d’ADN comprenant un promoteur, un site d’initiation et un site de terminaison. Chez les eucaryotes, il faut compléter cette définition par la présence d’introns localisés à l’intérieur de la partie transcrite du gène. D’autre part, il existe chez les procaryotes des gènes organisés en opérons (voies métaboliques) et donnant des ARNm polycistroniques. Mais on trouve également des gènes de structure plus simple ne contenant, comme chez les eucaryotes, qu’une seule unité de traduction.
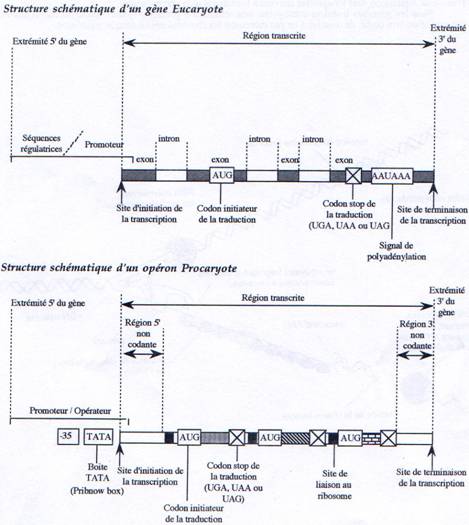
L’unité de transcription d’un gène correspond à la séquence présente dans le transcrit primaire d’ARN.
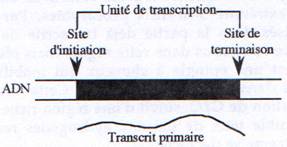
Chez les procaryotes comme chez les eucaryotes, la transcription est divisée en trois étapes initiation, élongation et terminaison.
I Transcription chez les procaryotes.
L’ARN polymérase ADN dépendante est une enzyme formée de plusieurs sous-unités le core-enzyme a la structure a2bb’ et l’holoenzyme a2bb’s chez E. coli. Elle polymérise les nucléotides dans le sens 5’à3’ à partir d’un promoteur. Cette enzyme n’a pas besoin d’amorce, n’utilise qu’un brin comme matrice et progresse à une vitesse d’environ 30 nucl./sec.A L’initiation.
L’initiation de la transcription se fait au niveau d’une séquence appelée promoteur. Ce promoteur est constitué de deux séquences très conservées, situées respectivement 35 et 10 pb en amont du site d’initiation de la transcription (+1).
Le core-enzyme a une affinité faible pour les séquences d’ADN double brin. Par contre la présence du facteur s dans l’holoenzyme confère à l’ARN polymérase une très forte affinité pour le promoteur. L’holoenzyme explore donc l’ADN par liaison non spécifique et se lie fortement aux régions promotrices qu’elle dénature localement pour commencer la transcription. L’initiation va durer le temps que la polymérase associe 7 ou 8 ribonucléotides sous forme d’un polymère hybridé au brin matrice. Comme le core-enzyme présente une très forte affinité pour les hétéroduplexes ARN/ADN, le facteur s se décroche et c’est le core-enzyme qui va seul continuer la transcription.
B L’élongation.
Le core-enzyme continue la polymérisation tout en déroulant l’ADN en aval et en le ré enroulant une fois la séquence copiée. En amont du site de polymérisation on trouve un hybride ARN/ADN d’environ 17pb.C La terminaison.
Aucune homologie de séquence n’a été retrouvée sur l’ADN au-delà du dernier nucléotide présent à l’extrémité 3’ d’ARN procaryotes. Par conséquent, les signaux de terminaison sont localisés dans la partie déjà transcrite de l’ARN. D’autre part, on ne retrouve pas de séquence consensus dans cette région mais plutôt une structure conservée.Cette structure est une épingle à cheveux qui mobilise les nucléotides de l’ARN normalement impliqués dans l’hybride ARN/ADN. Cette structure secondaire contient en général une forte proportion de G/C suivit d’une région riche en U. Le raccourcissement de l’hétéroduplexe et le faible taux de liaisons hydrogènes restant déstabilisent l’hybride ARN/ADN et le core-enzyme se décroche.
Certains terminateurs possèdent trop peu de G/C dans la région correspondant à l’épingle à cheveux pour que cette structure ne se forme pas. Un facteur supplémentaire (facteur r) va alors stabiliser cette structure secondaire. On parle dans ce cas de terminaison r dépendante par opposition aux terminaisons r indépendantes.
D Les ARNs polycistroniques.
Certains gènes procaryotes sont rassemblés en opérons structures qui renferment plusieurs gènes, impliqués dans une même voie métabolique, sous le contrôle d’un même promoteur. On retrouve donc au sein d’un même ARN, des séquences codant pour plusieurs protéines.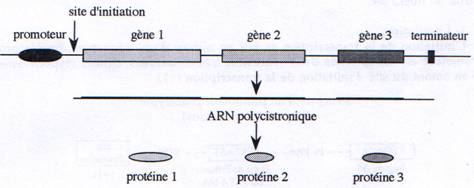
II Transcription chez les eucaryotes.
Il existe chez les eucaryotes trois ARN polymérases différentes:- ARN polymérase 1 : transcription des ARN ribosomiques
- ARN polymérase 2 : transcription des ARN messagers et ARNsn
- ARN polymérase 3 : transcription des ARN de transfert et des ARNr 5S.
Chez les eucaryotes le mécanisme de base de la transcription est identique à ce qui a été décrit pour les procaryotes. Cependant, la structure des promoteurs est différente et les transcrits primaires obtenus sont toujours monocistroniques. Enfin, une des différences majeures concerne les modifications post-transcriptionnelles des ARN eucaryotes;
ARNr (sauf le 5S) : méthylation, bases modifiées (par ex : U à yU-pseudoU) et épissage
ARNt : méthylation, épissage et bases modifiées (UàWU)
ARNr 5S : pas de modification
ARNm : coiffés, épissés et polyadénylés. Certaines adénines peuvent également être méthylées
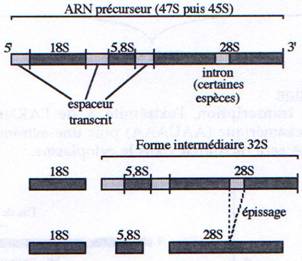
A Maturation des ARNr.
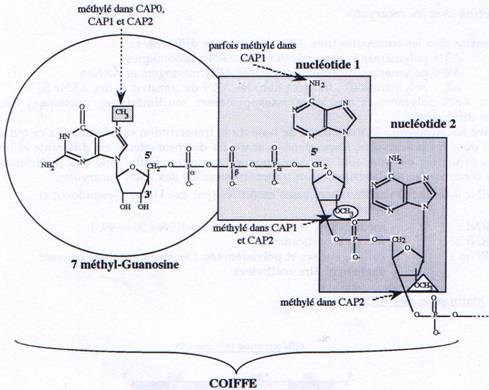
B Capping.
Au cours de la transcription, lorsque les ARNs atteignent 20 à 30 nucléotides de longueur, une 7 méthyl-guanosine est ajoutée sur le premier nucléotide en 5’, par une liaison phosphodiester 5’à5’. Tous les ARNm sont coiffés excepté les ARNm codant pour les histones. Il existe trois types de coiffes que l’on distingue en fonction de leur taux de méthylation- CAPO : seule la guanosine est méthylée en position 7
- CAP1 : CAPO + méthylation du C2’ du premier nucléotide et parfois de l’hétérocycle
- CAP2 : CAP1 + méthylation du CT du second nucléotide
C Polyadénylation.
A la fin de la transcription, l’extrémité 3’ de l’ARNm est clivé au niveau d’une séquence conservée hexamérique (AAUAAA) puis une extrémité poly A est rajoutée. Par la suite cette queue polyA sera raccourcie dans le cytoplasme.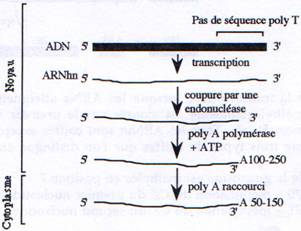
D Epissage.
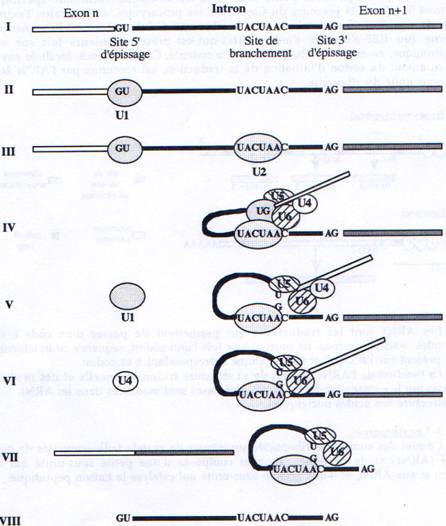
A la fin de la transcription, alors que le polyA vient d’être rajouté, les introns vont être éliminés. Les introns font donc partie du transcrit primaire et sont absents de l’ARN mature. Le mécanisme d’épissage se fait grâce à l’intervention de particules ribonucléo-protéiques appelées les snRNP (U1 à U6). Chacune de ces particules est formée d’un ARN et de plusieurs protéines. Un type d’épissage est décrit dans la figure ci dessous :- I : Structure du transcrit primaire
- II : U1 reconnaît le site 5’ d’épissage par interaction ARN/ARN ;
- III : U2 reconnaît le site de branchement par le même type d’interaction ;
- IV : l’hétérotrimère U4/U5/U6 se lie. U5 reconnaît le site 5’ d’épissage. U6 interagit
- V : U1 se dissocie. U5 se déplace de l’exon à l’intron.
- VI : U4 se dissocie. U6 catalyse la trans-estérification – le site 5’ d’épissage est coupé et le lasso est formé.
- VII : Le site 3’ d’épissage est coupé et les deux exons ligaturés. L’ARN épissé est libéré.
- U2/U5/U6 restent accroché sur le lasso.
- VIII : Le lasso est “débranché”
Chapitre Suivant:
